1047개 뇌 조직 단일 세포 데이터와 유전체 정보 통합 분석유전 변이 작동원리 규명 … 기존보다 최대 10배 많은 유전조절신호 포착특정 세포 표적 치료 전략 제시 … 美아이칸 의대 공동연구유전학 분야 세계적 권위지 '네이처 제네틱스'에 게재
-

- ▲ 성균관대 삼성융합의과학원/삼성서울병원 원홍희 교수(왼쪽)와 장범진 연구원(제1저자).ⓒ성균관대
성균관대학교는 삼성융합의과학원·삼성서울병원 원홍희 교수 연구팀이 단일 세포 수준에서 유전 변이가 뇌 질환에 영향을 미치는 정밀한 메커니즘을 규명했다고 27일 밝혔다.이번 연구는 복합적인 뇌 질환의 원인을 세포 단위에서 체계적으로 밝혀내 정밀 의료 시대를 앞당길 중요한 자산으로 평가받는다.이번 연구는 미국 뉴욕 아이칸 의과대학(Icahn School of Medicine at Mount Sinai) 타우피크 라즈 교수 연구팀과 공동으로 진행했다.그동안 과학계에선 ‘전장 유전체 연관성 분석(GWAS)’ 기법을 통해 질병과 연관된 수백만 개의 유전 변이를 찾아내 왔다. 그러나 이런 변이들이 구체적으로 어떤 유전자를 통해, 우리 몸속의 어떤 세포에서 작용해 병을 일으키는지는 베일에 싸여 있었다. 기존 연구들은 여러 종류의 세포가 섞여 있는 조직 전체의 평균값(Bulk level)을 분석했기 때문에 각 세포가 가진 고유한 특성과 이질성을 파악하는 데 한계가 있었다.연구팀은 이를 해결하기 위해 1047개 샘플의 대규모 뇌 조직 단일세포 데이터와 유전체 정보를 결합한 분석 체계를 구축했다. 단일 세포 수준에서 유전자의 발현을 조절하는 유전 변이(eQTL)를 정밀 분석한 결과, 기존 방식보다 3~10배에 이르는 방대한 세포 유형별 유전 조절 신호를 새롭게 규명하는 데 성공했다. -
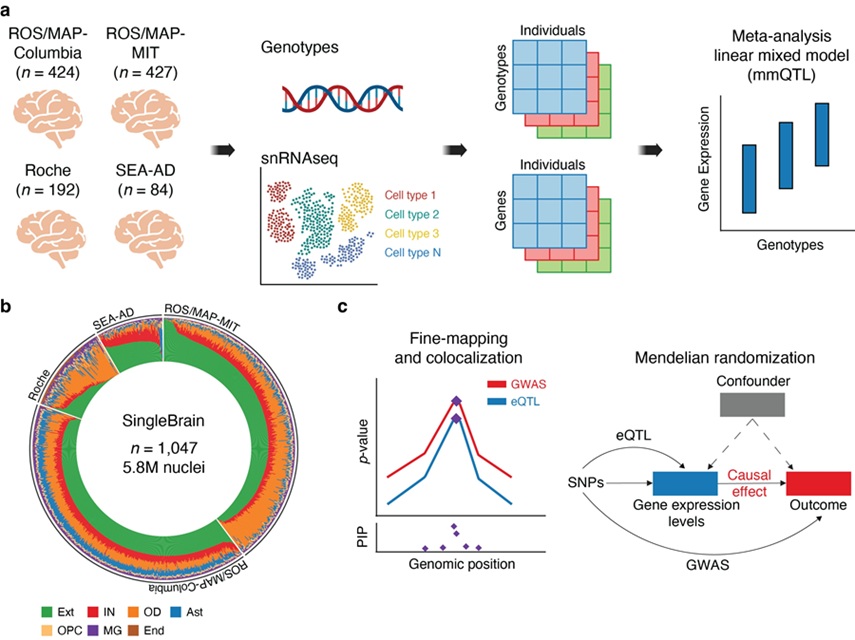
- ▲ 1047개 뇌 조직 단일세포 데이터와 유전체 정보를 결합한 SingleBrain 분석 결과.ⓒ성균관대
연구 결과의 핵심은 같은 유전 변이라도 세포의 종류에 따라 그 역할이 완전히 달라질 수 있다는 점이다. 연구팀은 뇌 질환과 밀접하게 연관된 유전 변이들이 뇌의 면역세포와 신경 세포에서 집중적으로 관여하고 있음을 확인했다. 또한 질병의 종류에 따라 특정 세포가 전혀 다른 기능적 결과를 유도한다는 사실을 밝혀냈다. 뇌 질환의 유전적 원인을 이해하기 위해 반드시 세포 수준의 정밀한 접근이 필요함을 과학적으로 입증했다.연구팀은 이번 분석을 통해 질병과 관련된 유전 변이가 실제 유전자 발현 변화로 이어지는 과정을 후성유전체 데이터를 통해 정밀하게 해석했다. 이를 기반으로 다양한 질환 사이에 공유되는 핵심 유전자 네트워크를 도출하고, 서로 다른 질병 간의 유전적 상관관계를 규명하는 등 뇌 질환 연구의 새 지평을 열었다는 평가다.원 교수는 “이번 연구는 뇌 조직과 세포 유형을 면밀히 분석해 유전 변이가 실제로 어떤 세포에서 작용하는지를 규명함으로써 뇌신경 질환의 원인을 파악하는 ‘해상도’를 한 단계 끌어올렸다”며 “앞으로 단일세포 기반 유전체 분석은 정밀 의료 구현의 핵심 도구로서, 특정 세포를 표적으로 하는 새로운 치료 전략을 세우는 데 중요한 단서를 제공할 것”이라고 했다.이번 연구 성과는 유전학 분야의 세계적 권위지 ‘네이처 제네틱스(Nature Genetics·네이처 유전학)’에 지난 19일 온라인 게재됐다. 장범진 연구원이 제1저자로 참여했다.이번 연구는 과학기술정보통신부 한국연구재단 바이오·의료기술개발사업의 지원을 받아 수행됐다. -

- ▲ 성균관대학교 전경. 좌측 상단은 유지범 총장.ⓒ성균관대